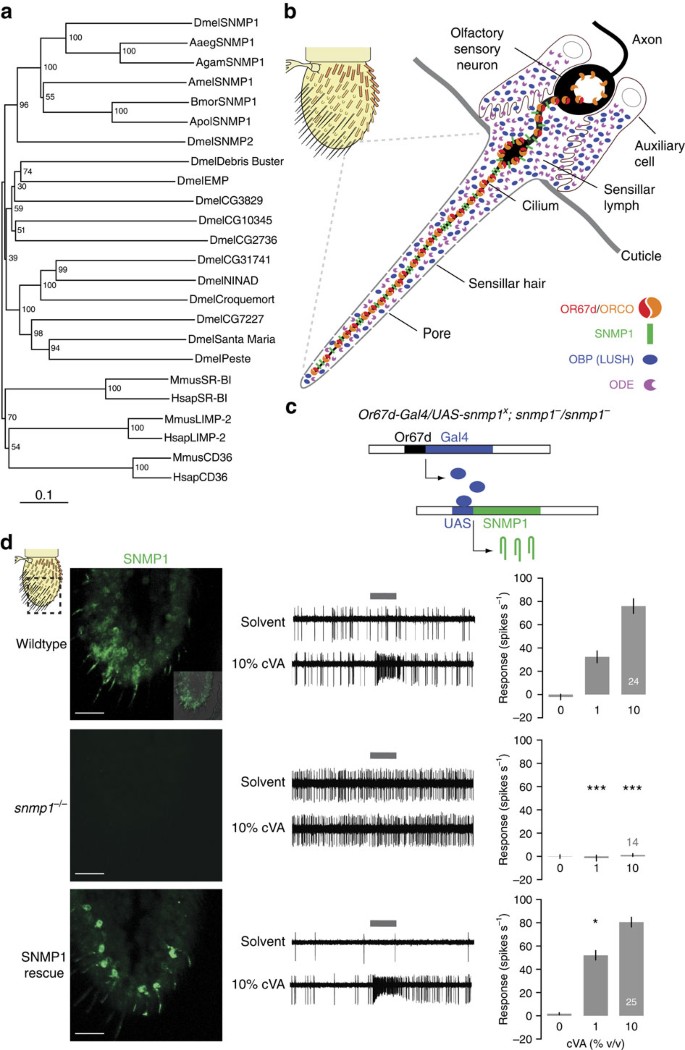
méthode neighbor joining
|
Cours de phylogénie moléculaire
En choisissant la méthode Distance puis le lien Distmat construisez votre arbre La méthode du Neighbor – Joining (NJ) Développée par Saitou et Nei (1987) |
|
Inférence phylogénétique
Neighbor-Joining Choisir deux objets i j garantis d'être voisins dans un Est-ce que cette différence est due à la méthode ou à la faiblesse du signal |
|
Introduction aux méthodes pour la phylogénie moléculaire
pdf Page 2 2 La phylogénie universelle ARNr petite sous-unité Barns et al Neighbor-Joining: calcul des longueurs des branches Branches périphériques i |
|
Le Neighbor-Joining (NJ)
Méthodes de distances • Il existe de nombreuses méthodes de reconstruction de distances – Méthode des moindres carrés • Minimise la différence entre la |
|
Méthodes de distance
Méthode de distances actuellement la plus utilisée : la neighbor joining (NJ) et ses variantes L'objectif des méthodes de distance : distances d'arbre (ou |
|
Neighbor Joining Method
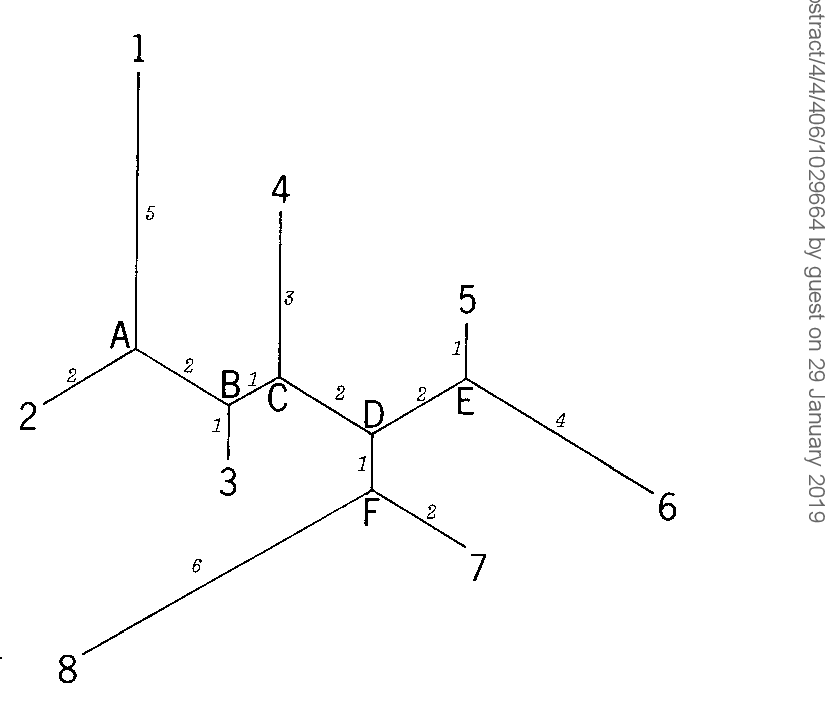
The Neighbor-joining Method: A New Method for Reconstructing Phylogenetic Tree Naruya Saitou2 and Masatoshi Nei ; Mol Biol Evol 4(4):406-425 1987 |
|
Nouveaux algorithmes pour linférence de réseaux phylogénétiques
The neighbor-joining method : a new method for reconstructing phylogenetic trees Molecular Biology and Evolution 4(4) 406–425 • Schwarz G et Gideon E |
|
Phylogénie moléculaire
Méthode du Neighbor Joining (Saitou et Nei 1987) Modélisation de l'hétérogénéité des vitesses d'évolution (Yang 1994) Premi`ere phylogénie construite |
|
Phylogénies
6 fév 2023 · □ Neighbor-joining □ Bio-Neighbor-joining □ Méthodes basées sur les changements d'états de caractère □ Méthode basée sur la parcimonie |
|
The Neighbor-joining Method
A new method called the neighbor-joining method is proposed for reconstructing phylogenetic trees from evolutionary distance data |
|
Le Neighbor-Joining (NJ)
Méthodes de distances. • Il existe de nombreuses méthodes de reconstruction de distances. – Méthode des moindres carrés. • Minimise la différence entre la |
|
Aucun titre de diapositive
Méthode de distances actuellement la plus utilisée : la neighbor joining. (NJ) et ses variantes. L'objectif des méthodes de distance : distances d'arbre (ou |
|
Introduction aux méthodes pour la phylogénie moléculaire
=> une méthode approchée (heuristique) est nécessaire. => Neighbor-Joining est une heuristique de “Evolution Minimale” La procédure de bootstrap n'aide pas à ... |
|
TD4 - Phylogénie
La topologie est-elle en accord avec vos observations sur l'alignement ? b) Construisez l'arbre selon la méthode du neighbor-joining avec les options : global |
|
Diapositive 1
The neighbor-joining method : a new method for reconstructing phylogenetic trees. Molecular. Biology and Evolution 4(4) |
|
Phylogénie - Informatique Génomique - Master 1
Méthodes fondées sur les distances. NJ(Neighbor-Joining). ▻ Méthode – Saitou et Nei (1987) – tentant de corriger UPGMA afin d'autoriser un taux de mutation |
|
Revue Ezzaitouna 16 (1) 2020
phylogénétique non enraciné par la méthode de Neighbor-Joining (NJ) (Saitou et Nei1987) |
|
Méthodes de reconstruction des Phylogénies
Neighbor Joining (NJ). (Saitou and Nei Mol. Biol. Evol. 1987). Dans un arbre non raciné |
|
Applications des méthodes phylogénétiques en linguistique.
17 janv. 2017 The neighbor-joining method : a new method for reconstructing phylogenetic trees. Molecular Biology and Evolution 4(4) |
|
Méthodes efficaces pour reconstruire de grandes phylogénies
10 juil. 2013 Le critère d'agglomération utilisé par l'algorithme Neighbor Joining (NJ) introduit par. (Saitou et Nei 1987) repose sur l'idée que l'évolution ... |
|
Le Neighbor-Joining (NJ)
Famille majeure de méthodes phylogénétiques Le terme Neighbor (=voisin) désigne 2 taxa ... Algorithme du Neighbor-Joining. |
|
Introduction aux méthodes pour la phylogénie moléculaire
La plupart des méthodes phylogénétiques produisent des arbres non racinés. Neighbor-Joining est une heuristique de “Evolution Minimale” ... |
|
The Neighbor-joining Method: A New Method for Reconstructing
Key words: phylogenetic tree neighbor-joining method |
|
PHYLOGENIE DES URSIDES Lycée
La méthode UPGMA (Unweighted Pair Group Method with Arithmetic Mean) est La méthode du Neighbour Joining (Neighbor Joining- NJ) est aussi une méthode de. |
|
Une nouvelle méthode efficace pour la reconstruction des arbres
neighbor-joining de Gascuel [GAS 97]. Cependant le problème de la reconstruction des arbres ultramétriques et additifs à partir des matrices de distances |
|
Utilisation des arbres phylogénétiques dans lalignement de séquence
une méthode exacte que pour des séquences de petites tailles et dont le nombre concevoir Les arbres phylogénétiques avec l'algorithme Neighbor Joining ... |
|
TD4 - Phylogénie
b) Construisez l'arbre selon la méthode du neighbor-joining avec les options : global gap removal (valeur par défaut) observed divergence |
|
Analyses bioinformatique et phylogénétique des gènes nod et nif de
22?/06?/2014 méthode de Neighbor-joining (NJ) en utilisant les paramètres de correction de Kimura. La robustesse des phylogrammes à été évaluée à l'aide ... |
|
Applications des méthodes phylogénétiques en linguistique.
17?/01?/2017 Neighbor-Joining (NJ). • Méthode développée par Saitou et Nei (1987). • Méthode de distances la plus utilisée. |
|
Étude morphologique et phylogénétique dune souche actinomycétale
Figure 7 : Arbre selon la méthode des distances (Neighbor-joining) montrant la position phylogénétique de la souche N18 parmi les 30 espèces type |
|
The Generalized Neighbor Joining method - University of Kentucky
Neighbor Joining with Subtree Weights Input: n DNA sequences and an integer 2 ? m ? n?2 Output: A phylogenetic tree T with n leaves 1 Compute all m-subtree weights via the ML method 2 Compute S(ij) for each pair of leaves i and j 3 Apply Neighbor Joining method with a tree metric S(ij) and obtain additive tree T? 4 |
Is the neighbor-joining method better than the other methods?
The new, neighbor-joining method and Sattath and Tversky's method are shown to be generally better than the other methods. Many plant-parasitic fungi have an ability to grow saprophytically for at least a part of their life cycle. Thus they are not completely dependent on an environment favorable to their plants.
What is neighbor-joining method in phylogenetic inference?
The neighbor-joining (NJ) method is widely used in reconstructing large phylogenies because of its computational speed and the high accuracy in phylogenetic inference as revealed in computer simulation studies.
What is neighbor joining?
Neighbor joining is similar to UPGMA/WPGMA, but infers unrooted trees. As a consequence, and unlike UPGMA/WPGMA, it does notrequire that the multiple sequence alignment (MSA) has been generated according to a molecular clock along an ultrametric tree. There are a few differences from UPGMA/WPGMA. Choosing which nodes to merge
What is a neighbor-joining heuristic algorithm?
A "ddivide-and-conquer" heuristic algorithm in which an initial neighbor-joining (NJ) tree is divided into subtrees at internal branches having bootstrap values higher than a threshold, which is suitable for reconstructing relatively large molecular phylogenetic trees. FastJoin, an improved neighbor-joining algorithm.
| Le Neighbor-Joining (NJ) - Université Paris-Saclay |
| The Generalized Neighbor Joining method - University of Kentucky |
| Neighbor joining algorithm - University of Helsinki |
| Construction of Phylogenetic Tree using Neighbor Joining Method |
| Neighbor-Net: An Agglomerative Method for the Construction of |
| Searches related to méthode neighbor joining filetype:pdf |
|
13 LADN ribosomique - Bibliothèque et Archives Canada
1 2 4 3 1 Le neigh bor-joining La méthode du neighbor-joining a été proposée par Saitou et Nei en 1987 Elle fut inspirée de celle proposée par Fitch et |
|
BACHELORARBEIT - MOnAMi - Publication Server of Hochschule
3 3 Die Neighbor-Joining Methode Der Neighbor-Joining-Algorithmus (NJ) ist ein 1987 von Naruya Saiou und Masatoshi Nei entwickeltes mathematisches |
|
6 Distanzverfahren
6 4 2 Neighbour Joining: NJ 198 6 5 Geringe Distanz zur In mancher Beziehung dem GTR-Modell überlegen, hat die Methode aber unter anderem den |
|
Correspondence of function and phylogeny of ABC proteins based
27 oct 2005 · known human ABC proteins and used neighbor- joining tree estimation All but 11 the neighbor-joining algorithm 22,50 Note that the sec- ond copies of Pérez AJ, Rodrıguez A, Trelles O, Thode G A computational strategy |
![PDF] The neighbor-joining method: a new method for reconstructing PDF] The neighbor-joining method: a new method for reconstructing](https://i1.rgstatic.net/publication/12212552_Efficiency_of_the_Neighbor-Joining_Method_in_Reconstructing_Deep_and_Shallow_Evolutionary_Relationships_in_Large_Phylogenies/links/540f6b630cf2f2b29a3dde48/largepreview.png)


![PDF] The neighbor-joining method: a new method for reconstructing PDF] The neighbor-joining method: a new method for reconstructing](https://d3i71xaburhd42.cloudfront.net/579de0a16edb6b1ebb14adb720933527881cc18f/5-Table1-1.png)
![PDF] The neighbor-joining method: a new method for reconstructing PDF] The neighbor-joining method: a new method for reconstructing](https://d3i71xaburhd42.cloudfront.net/579de0a16edb6b1ebb14adb720933527881cc18f/10-Figure6-1.png)
![PDF] The neighbor-joining method: a new method for reconstructing PDF] The neighbor-joining method: a new method for reconstructing](https://upload.wikimedia.org/wikipedia/commons/thumb/c/cf/Neighbor_joining_7_taxa_start_to_finish_diagram.svg/400px-Neighbor_joining_7_taxa_start_to_finish_diagram.svg.png)

![PDF] The neighbor-joining method: a new method for reconstructing PDF] The neighbor-joining method: a new method for reconstructing](https://i1.rgstatic.net/publication/45865450_The_Geometry_of_the_Neighbor-Joining_Algorithm_for_Small_Trees/links/5409a9ce0cf2718acd3f44fa/largepreview.png)


![PDF] The neighbor-joining method: a new method for reconstructing PDF] The neighbor-joining method: a new method for reconstructing](https://i1.rgstatic.net/publication/221313447_Rapid_Neighbour-Joining/links/00b4953734428e3e50000000/largepreview.png)

![PDF] The neighbor-joining method: a new method for reconstructing PDF] The neighbor-joining method: a new method for reconstructing](https://d3i71xaburhd42.cloudfront.net/579de0a16edb6b1ebb14adb720933527881cc18f/13-Table5-1.png)
![PDF] The neighbor-joining method: a new method for reconstructing PDF] The neighbor-joining method: a new method for reconstructing](https://d3i71xaburhd42.cloudfront.net/579de0a16edb6b1ebb14adb720933527881cc18f/15-Table6-1.png)
![PDF] The neighbor-joining method: a new method for reconstructing PDF] The neighbor-joining method: a new method for reconstructing](https://onlinelibrary.wiley.com/cms/asset/eabd1071-1a5d-4e8e-af47-51ac5a93294c/cla12205-fig-0011-m.jpg)